基因芯片BSA结合KASP单标记快速精细定位基因
导语
我国作物品种资源丰富,含有大量与产量、品质、抗性以及营养高效利用等相关的诸多优良性状。但是如何在如此多的性状中找到那些和育种紧密相关的关键优质基因一直是农业科学研究的重点。基因定位是基因克隆、表达调控、选择进化等研究的基础,更是对分子标记辅助育种等促进和加速改良作物发展的技术具有重要意义。
今天就为大家介绍一种基因芯片BSA结合KASP单标记快速精细定位基因的方法。
BSA(Bulked Segregation Analysis)即集团分离分析法,一种利用分离群体中的极端单株组成的混池快速进行基因定位的方法。也是如今基因定位研究领域使用最多的一种方法。
利用双绿源基因芯片开展BSA基因定位,只需要两个亲本+两个混池,最快一周就能快速进行水稻、油菜、玉米、番茄的功能基因初定位。
基因芯片BSA定位的原理是从一个分离群体中选择在目标性状上的表型处于两个极端的若干单株(一般情况下两个极端表型分别选取20-40个单株)构建两个DNA混合池,通过利用高密度的SNP芯片检测分析两个混合池与亲本在基因指纹上的差异,定位到与表型相关联的基因区段。

二:基因芯片BSA操作的流程

三:基因芯片BSA的注意事项
BSA定位的效果与很多的因素有关。例如亲本的纯度、表型的复杂程度以及混池单株表型鉴定的准确性等。具体注意事项详见双绿源公众号之前发表的专题文章。
1.两个亲本+两个混池,最快一周,BSA定位,就用双绿源基因芯片
2.做BSA基因定位,极端单株的表型选取到底有多重要,看这个案例就知道了!
BSA定位虽然因其高效、简单、快速、经济的优点在基因定位领域广受欢迎,但BSA属于初定位,定位到的区间一般较大,很难在定位的区段内直接筛选到真正调控目标性状的基因,这时候就需要在我们初定位的区段内设计单标记筛选重组单株,缩小定位区段。
而KASP技术是一种基于荧光检测的新型基因分型技术,能够在复杂的基因组DNA样品中对特定位点上的SNP和插入缺失序列进行精准的双等位基因检测。KASP相较于传统的SSR等标记,具有标记丰富,多态性高,灵活、便宜、准确性高、通量高等特点。
结合我们的作物SNP基因芯片,将初定位区间内的芯片特异性SNPs转化为KASP标记。十分适合在基因芯片BSA初定位后利用混池群体通过KASP标记筛选重组单株从而缩小定位区间。
对于定位范围较大,基因芯片在缩小的定位区间内标记数目较多的情况,通过芯片检测重组单株,5个工作日即可进一步缩小定位区间。
利用芯片进行BSA结合KASP单标记进行基因定位,对比传统的QTL定位以及高通量测序等手段,在保障定位精细度的同时,降低了定位的周期与成本,节省了经费与时间。
二:BSA初定位
从两个混池中各挑选30株极端单株取混样连同双亲共计4个样品进行基于芯片的BSA分析。结果如图,混池1与SLY1表型相同为隐性表型,筛选混池1纯合且与混池2有差异的位点。可以判定目标基因可能位于8号染色体14.75-26.70 Mb之间。
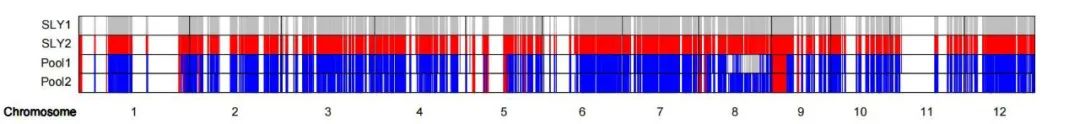
由于初定位的区段较大,将近12 Mb,其中双亲纯合且有多态性的芯片探针有390个,下一步利用这些探针每隔2-3 Mb设计KASP单标记4个。
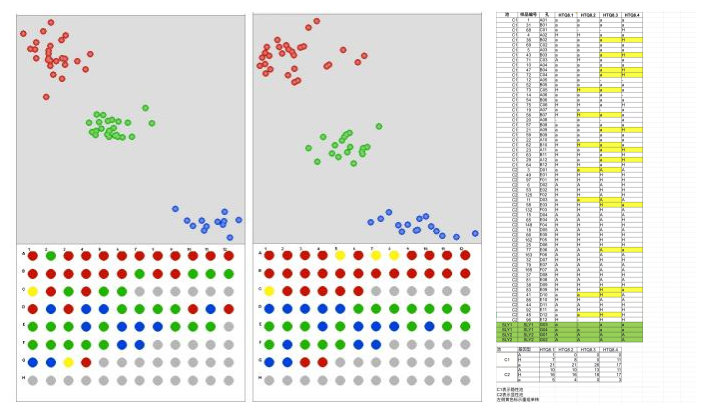
KASP分型部分结果如上图所示,从60株极端单株群体中共筛选到17株关键重组单株,同时KASP结果也将定位区间缩小到8号染色体20.69-24.70MB之间。
挑选两种极端表型单株各2株共4株重组单株进行芯片检测,结合亲本进行背景分析,放大定位区间分析。
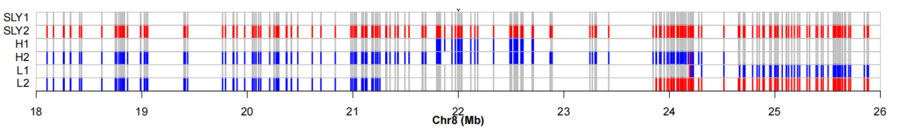
已知亲本SLY1与重组单株L1与L2表型一致且为隐性,亲本SLY2与单株H1,H2表型一致且为显性。结合背景分析通过关键单株H1缩小定位区间到8号染色体21.79-22.75 Mb之间,约1 Mb大小。
案例仅10个工作日通过4个KASP标记筛选重组单株,加上芯片检测4株重组单株,就将基因定位范围缩小了近12倍。


